
文章提供:創源生技
3. 更快查看 Core Analysis 的結果
現在您可以在 Core Analysis 開始處理後立即打開它並在分析結果可開啟時立即查看。當數據進行 Core Analysis 分析後,就可以馬上在 Project Manager 點擊查看。如果分析的圖標有一個時鐘,則表示該分析正在排隊等待處理,並且當您打開它時,您會看到它在排隊中的位置。一旦開始分析,圖標會逐漸充滿綠色表示完成進度。這時會出現單獨的分析分頁,例如 Canonical Pathways 等等,一旦完成分析,這些分頁名稱將會從灰色字體變成黑色字體。這時就可以開始查看您的分析結果。
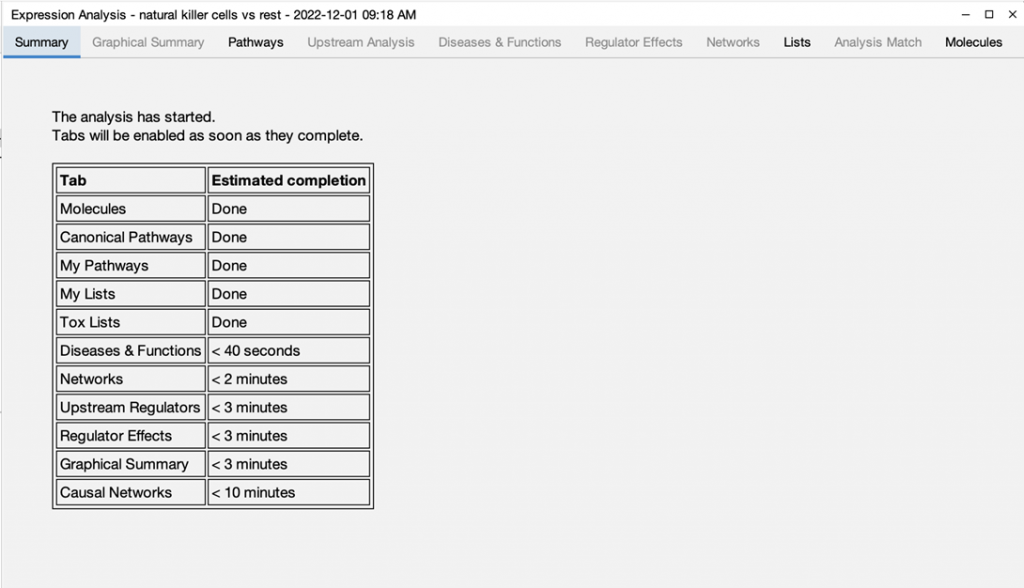
上排不同的分析分頁顯示它們目前的狀態。分析完成後會由灰色字體變為黑色字體。
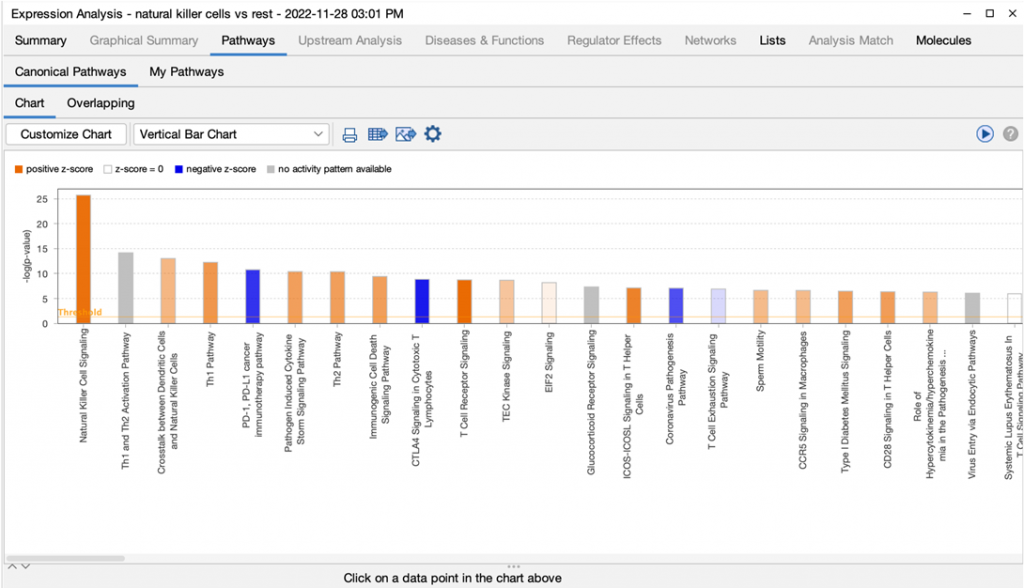
可以立即查看已分析好的分頁資訊,即使其他分頁的分析還沒完成(呈現灰色字體)。
4. 改善了水平直條圖以用於發表
期刊發表更喜歡數據的緊密呈現以節省期刊中的頁面空間。現在,當直條圖以水平方向呈現時,直條的間隔顯示得更緊密,如圖六所示。
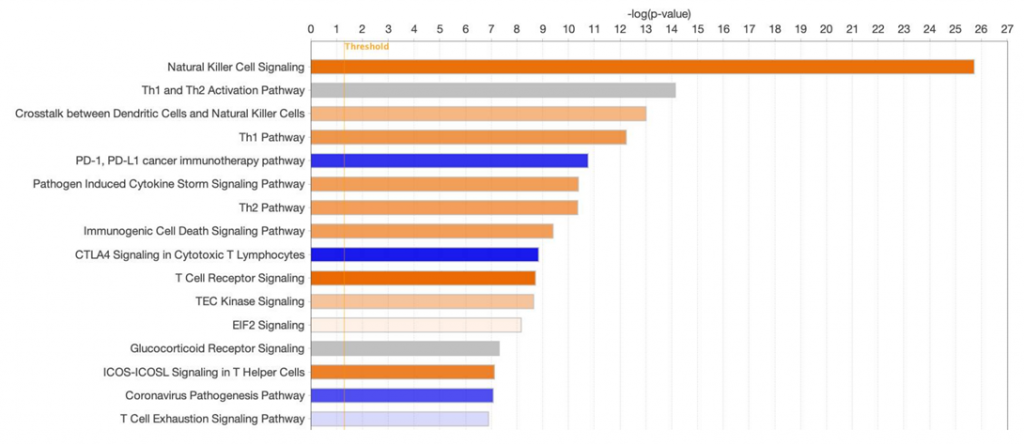
5. Core Analysis 分頁的節省空間排列
在此版本中,Core Analysis 中的某些分頁已得到整合,更加直觀和節省空間。Canonical Pathways 分頁和 My Pathways 分頁已作為子分頁匯集到一個新的“Pathways”分頁,Molecules 分頁已移至最右側。現在在預設的情況下不需要放大就可以看到所有的Core Analysis分頁。
6. 更快地從網路圖和路徑圖連結至Gene Views, Chem Views, and Disease Views
現在您可以右鍵點擊路徑圖或網路圖中的任何節點以查看其相應的Gene Views, Chem Views, and Disease Views網頁。圖七顯示了右鍵點擊基因節點並選擇“View Details”。這將在您的預設網絡瀏覽器中顯示其Gene View頁面。

7. 資料庫更新
New pathways
- Chaperone Mediated Autophagy Signaling Pathway
- IL-33 Signaling Pathway
- Myelination Signaling Pathway
- NOD1/2 Signaling Pathway
Existing pathways updated to include an activity pattern
- Adipogenesis pathway
- Chronic Myeloid Leukemia Signaling
- IL-12 Signaling and Production in Macrophages
- Mitochondrial Dysfunction
Addition of ~120,000 new findings (bringing the total in IPA to over 12 million)
~96,000 Expert findings ~10,000 protein-protein interaction findings from BioGrid
~8,000 cancer mutation findings from ClinVar
~4,000 Gene Ontology findings
~1,200 target-to-disease findings from ClinicalTrials.gov
~1,200 drug-to-disease findings from ClinicalTrials.gov
~150 gene to disease or phenotype associations from the Mouse Genome Database (MGD or "Jax”)
~200 newly mappable chemicals
Identifier mapping support added for two new species
- Atlantic Salmon (Salmo salar)
- Sheep (Ovis aries)
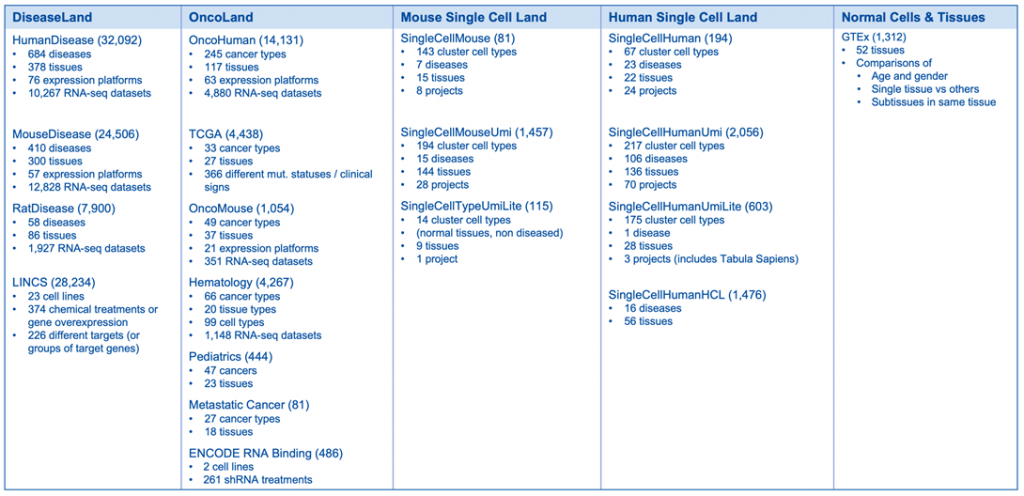
124,927 expression datasets will be available in early January 2023 (3,177 added)

Breakdown of the OmicSoft datasets by Land (early January 2023)
Gene model source versions
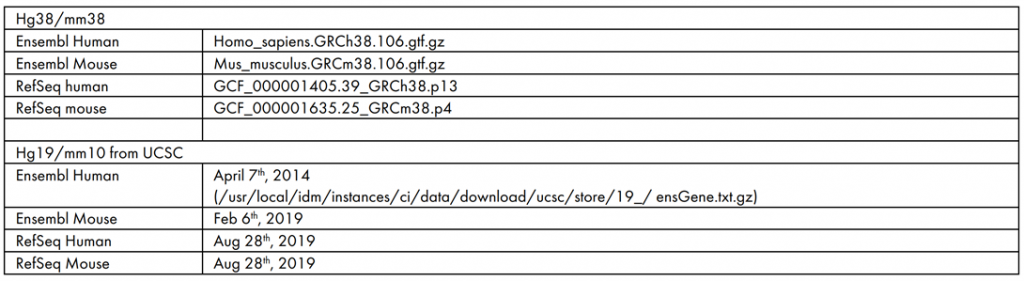
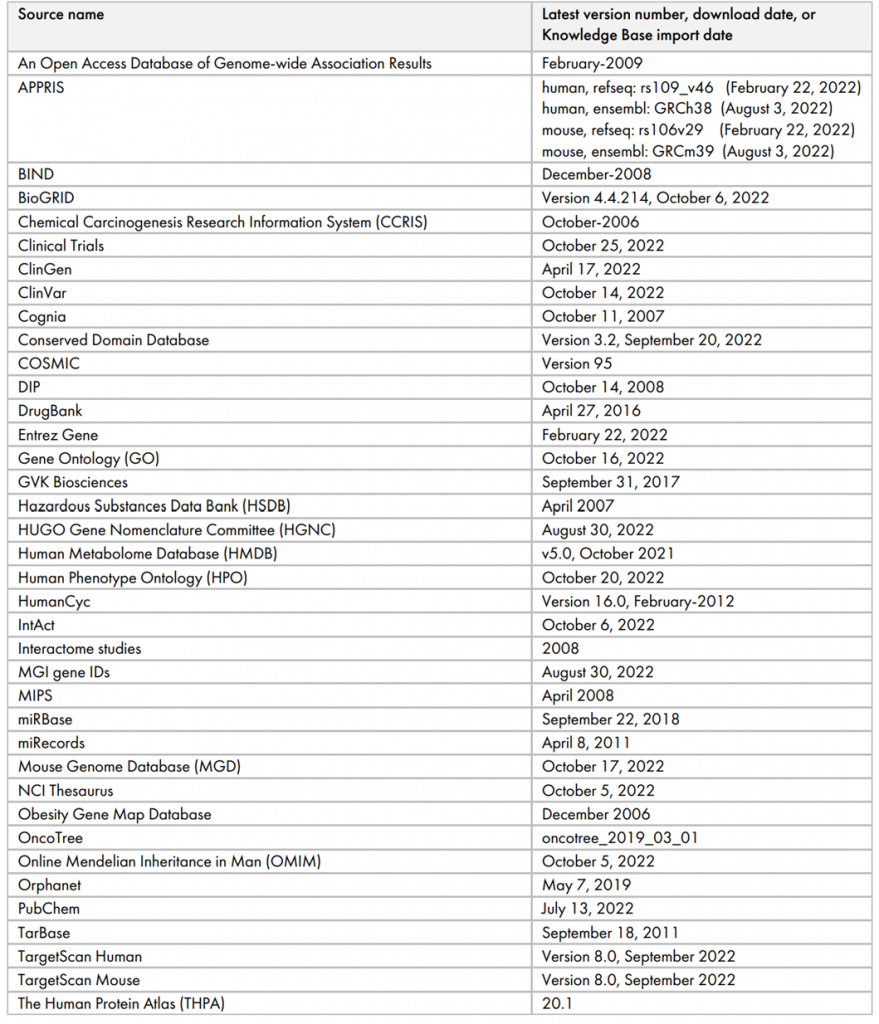
Version and/or date of third-party databases (update until 2022/12/20)
若有需要進一步的資訊,或在使用軟體上遇到問題,歡迎聯繫以下窗口:
徐竹君 業務專員 LenaHsu@GGA.ASIA 02-2795 1777 #3013
黃柔諭 產品專員 ZoeHuang@GGA.ASIA 02-2795 1777 #3024